Программа для просмотра dicom для linux

DICOM stands for Digital Imaging and Communications in Medicine and it is the international open image format for handling, storing, printing, and transmitting information in medical images.
Medical images are used in the identification and examination of physical injuries and diseases via procedures like Xrays, CT scans, etc.
This article lists the best free Linux applications used for processing images generated by DICOM devices.
1. Amide
Amide is a cross-platform GTK+ tool for viewing, registering, and analyzing volumetric medical imaging data sets. It uses a GUI with a long feature list including loading multiple data sets at once, generating fly through movies as MPEG1 files, an anisotropic filtering wizard, thresholding datasets independently and in bulk, etc.
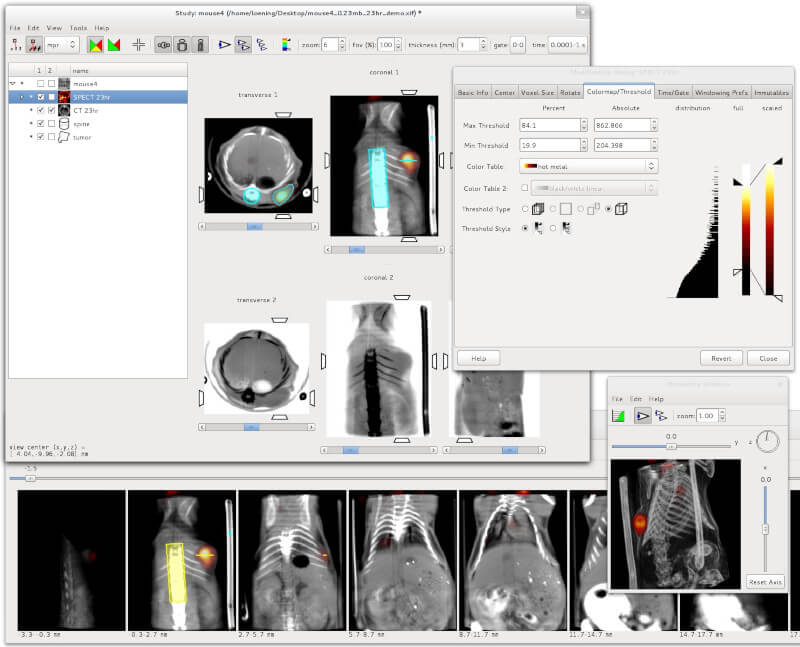
AMIDE – Medical Imaging Data Examiner
2. DicomBrowser
DicomBrowser is an open source Java-based DICOM metadata inspector and modifier app. It was developed by the Neuroinformatics Research Group of Washington University to be excellent at batch anonymizations.
It is cross-platform, can simultaneously load thousands of images, and also features a command line interface to the anonymization script engine.
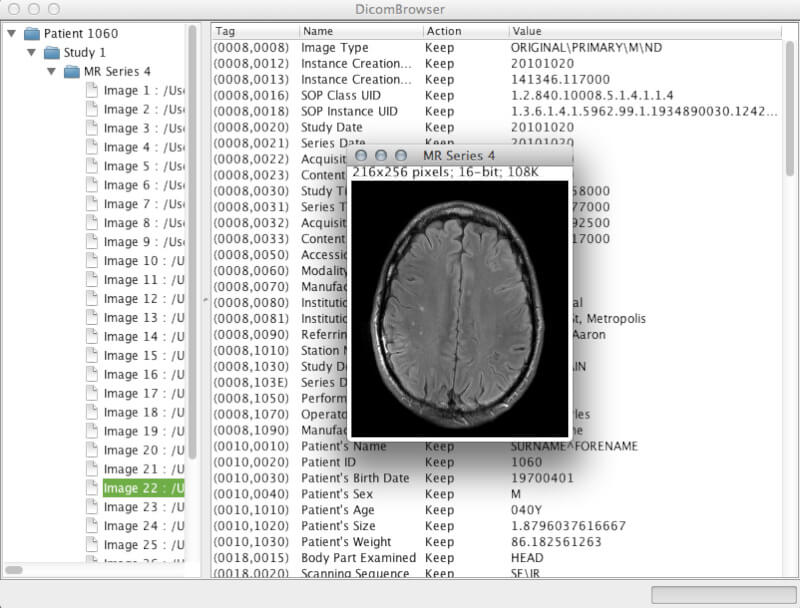
DicomBrowser – Viewing and Modifying DICOM Metadata
3. 3DimViewer
3DimViewer is a cross-platform lightweight 3D viewer for DICOM datasets written in C++. It is open source with a feature set that includes orthogonal and multiplanar XY, XZ, and YZ views, an adjustable density window, importing multiple DICOM datasets, 3D visualization of CT and MRI scans, surface modelling of any segmented tissue, 3D surface rendering, etc.
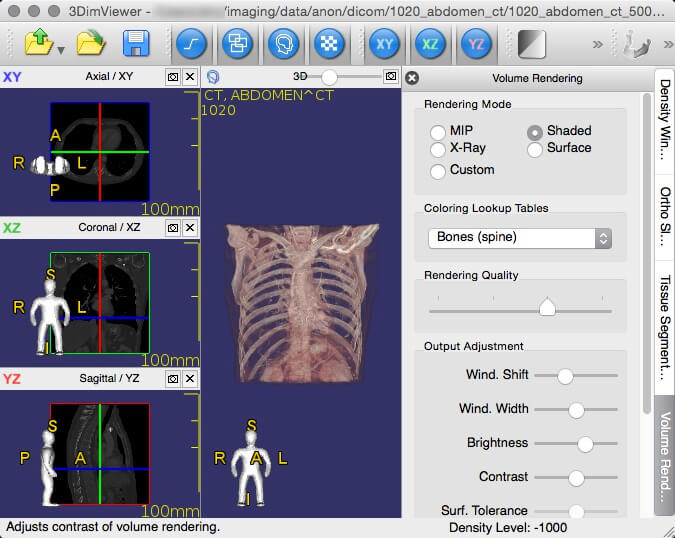
3DimViewer- 3D Viewer of Medical DICOM
4. dcm4che
Unlike the other titles on this list, dcm4che is a Java-based suite of high-performance applications collected for the healthcare enterprise and it is used worldwide by researchers and in both open source and commercial applications.
dcm4che enables you to store any DICOM object type in standard file systems with full support for Client/Server PACS model, DICOM IOD’s, multiple platforms, and several IHE integration profiles.
Its features also include a web-based GUI for administrators, an integrated HL7 server which can act on ADT, ORU, and ORM message types among others.

DCM4Che – A Collection of Apps for Healthcare IT
5. XMedcon
XMedcon is an open source medical image conversion toolkit and library developed mainly for converting reconstructed nuclear medical images.
You can use it to read unsupported files without compression, retrieve the raw binary/ASCII image arrays, to print pixel values, to write PNG for desktop applications, and to extract/reorder specified images among other functions.
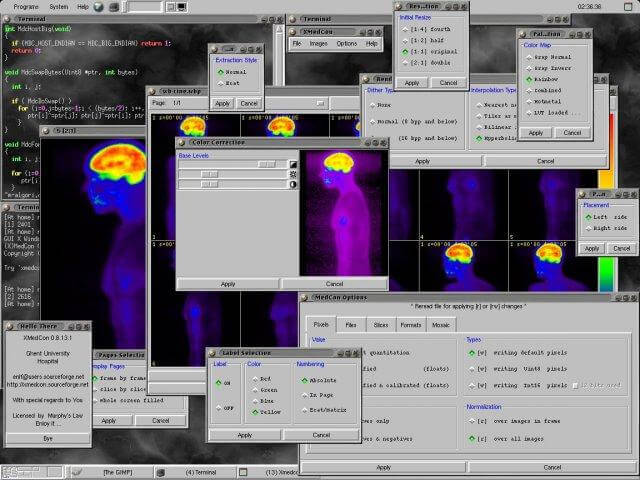
XMedcon – Medical Image Conversion Toolkit
6. Aeskulap
Aeskulap is a medical image viewer that was created to be an open source alternative to commercial DICOM viewers and is based on glademm, gtkmm, and gconfmm.
It can load a series of DICOM images for review and can also fetch them from archive nodes (aka PACS) over the network.
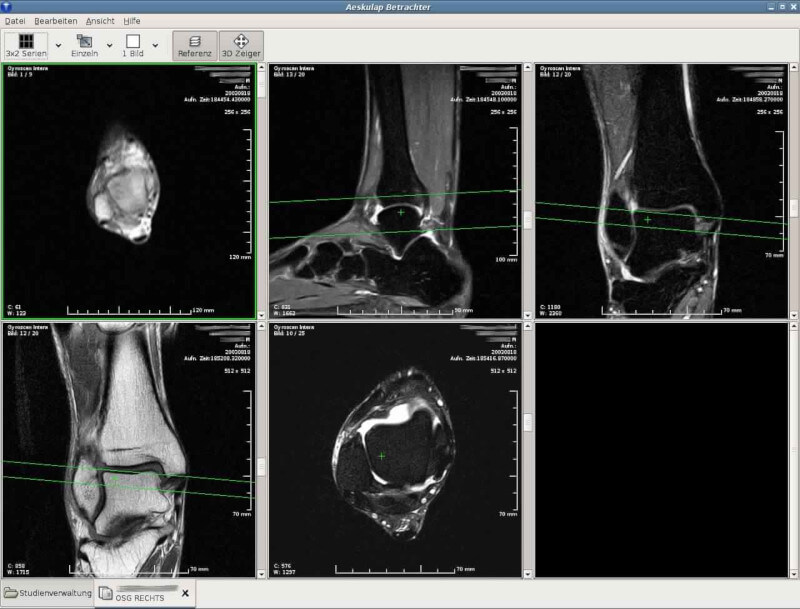
Aeskulap – DICOM Image Viewer
7. Mango
Mango stands for Multi-image Analysis GUI and it provides tools for image analysis coupled with a convenient GUI for navigation.
It can be used for ROI editing, image stacking, statistical analysis, surface rendering, etc. You can also customize filters, colour tables, file formats, work with plugins, and analyse other image formats such as MINC, NEMA-DES, NIFTI and NIFTI2.
Mango – Multi-image Analysis GUI
8. 3D Slicer
3D Slicer is a feature-rich multi-platform integrated application for processing images, medical image informatics, and 3D visualization intended for clinical researchers, physicians, and computer scientists.
You can use 3D slicer for sophisticated manual editing, automatic segmentation, analysing and visualizing diffusion tensor imaging data, reading and writing DICOM images and other formats, batch processing using EMSegment BatchMake e.t.c filtration, among many other functions.

3D Slicer – Image Analysis and Scientific Visualization
9. SMILI
SMILI (pronounced ‘smilie’) is an open source lightweight and cross-platform library containing a set of classes for building medical image processing and scientific visualization applications.
It features both a simple GUI and a CLI with standard processing algorithms for smoothing, thresholding, masking etc. images and models.

SMILI – Simple Medical Imaging Library Interface
Its features include a tree view of ACR-NEMA and DICOM content, support of ACR-NEMA and DICOM images export to different image formats, image view with single and multiple frame support, image slide cycling known as movie mode, full DICOM 2007 data and UID dictionaries, etc.

11. Kradview
Kradview is an NMR, DICOM, and X-ray-compatible imaging device built for Unix-like platforms. Its purpose is to make rendering DICOM images easier irrespective of their size and zoom level.
It was initially developed by David Santo Orcero as part of his PhD project and has been updated by David del Rio Medina to have a better rendering performance.

Kradview – X-ray Image Viewer
Do you have any experience with the listed software above? Or perhaps you know other reliable titles that we can add to our list. Feel free to add your suggestions and questions in the section below.
DICOM (Digital Imaging and Communications in Medicine) is the international standard to transmit, store, retrieve, print, process, and display medical imaging information.

Note: This article is an Evergreen article. It will receive continues update about the listed applications. You can save it and return to it as a updated resource.
DICOM (Digital Imaging and Communications in Medicine) is the international standard to transmit, store, retrieve, print, process, and display medical imaging information. The Following is a list of the best free DICOM viewers for doctors.
We have covered several categories for DICOM viewers, here what we covered so far:
Free Online Web-based DICOM viewers are online cloud services that display upload or remote DICOM files or folders with DICOM specific browser. Here is a compiled list of cloud DICOM viewers.
In this article we have covered the best free and open source DICOM viewers for many platforms. This list is always updated with emerging and new software regularly, so stay tuned.
Free & Open source enterprise-grade DICOM viewers
1- Navegatium DICOM Viewer
Navegatium DICOM Viewer
Incredibly easy to use, Navegatium has an absolutely intuitive touchscreen interface, works perfectly on Windows 10 and Windows 8.1 tablets, laptops and PCs and can be installed directly from Windows Store. It makes out list of Best Free & Open source PACS Clients & DICOM Workstations, because of its outstanding features.
It is capable of 2D, 3D and X-Ray reconstructions with DICOM images.
We have written a snap preview about Nevegatium, you can read it here.
2- Sante DICOM Viewer Free version

Sante DICOM Viewer Free

Sante DICOM Viewer Free
Sante DICOM Viewer Free supports all the modalities (CT, MR, US, CR, NM, XA, MG, DX etc.), all the manufacturers, and all the DICOM file types (DICOM 3.0/NEMA 2).
3- MicroDicom: Free DICOM Viewer for Windows

MicroDICOM
MicroDicom is an application for primary processing and preservation of medical images in DICOM format.
It is equipped with the most common tools for manipulation of DICOM images, and it has an intuitive user interface. It is free for non-commercial use.
4- Horos DICOM Project: Open source DICOM viewer for Mac OSX
Horos DICOM
Horos is a free, open-source medical image viewer. The goal of the Horos Project is to develop a fully functional, 64-bit medical image viewer for OS X. Horos is based upon OsiriX and other open-source medical imaging libraries. Horos is made available under the GNU Lesser General Public License, Version 3 (LGPL-3.0).
Horos has been featured several times in our list reviews:
5- JiveX DICOM Viewer
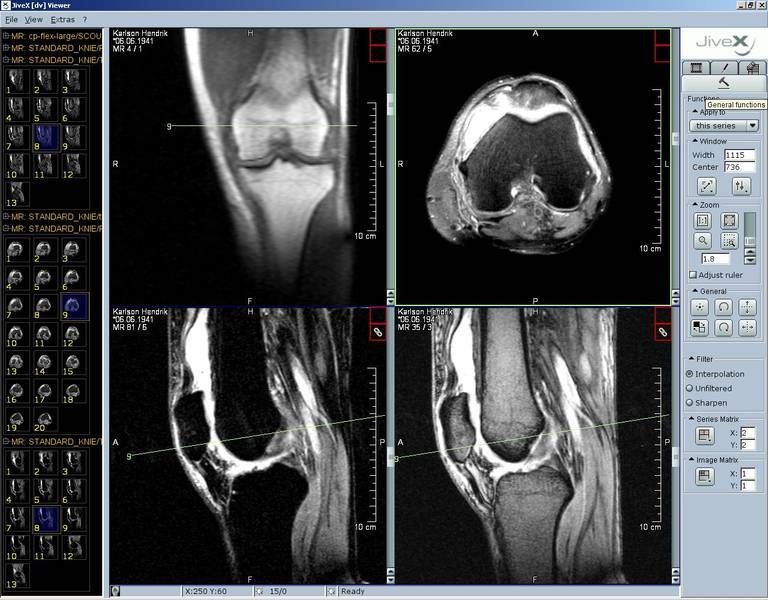
JiveX DICOM Viewer - src
This free DICOM Viewer offers not only to review radiology images but also other types of medical data such as ECGs or information in pdf files – as long as the data is available in DICOM format. Thus the DICOM Viewer provides all users with access to important information far beyond radiology.
Data can be loaded onto the Viewer from an internal folder or from external media such as CD, DVD or stick. Unlike the licensed Review Client the free DICOM Viewer cannot be linked to the PACS. Technical service is not included.
It is available for non-commercial use (research or educational purposes).
6- AMIDE: Open source Multi-platform DICOM workstation for Linux, Windows and Mac OSX
AMIDE is a completely free and open source tool for viewing, analyzing, and registering volumetric medical imaging data sets.
7- 3DimViewer
3DimViewer is a lightweight free and opensource 3D viewer of medical DICOM datasets that is distributed as open source software.

postDICOM: Online DICOM Viewer
postDICOM is a secure environment for patients, doctors, clinics and hospitals. Using postDICOM, users can Post medical DICOM images (computed tomography, magnetic resonance imaging, ultrasound, digital radiography etc.) and clinical documents (scanned documents, reports, patient’s history etc.) to cloud. Later, users can view and share these documents with doctors and medical groups. Uploaded DICOM files are streamed using sophisticated HTML5 zero footprint lossless DICOM viewer.
9- SMILI DICOM viewer
The Simple Medical Imaging Library Interface (SMILI), is an open-source, light-weight and easy-to-use medical imaging viewer and library for all major operating systems. The main sMILX application features for viewing n-D images, vector images, DICOMs, anonymizing, shape analysis and models/surfaces with easy drag and drop functions. It also features a number of standard processing algorithms for smoothing, thresholding, masking etc. images and models, both with graphical user interfaces and/or via the command-line. SMILI is in active development by his developers.
Mango – short for Multi-image Analysis GUI – is a viewer for medical research images. It provides analysis tools and a user interface to navigate image volumes.
Mango is available for use, as is, free of charge, for educational and scientific, non-commercial purposes. Mongo also made it in our featured list as one of the : Best Free & Open source PACS Clients & DICOM Workstations for Windows, Mac OSX, & Linux.
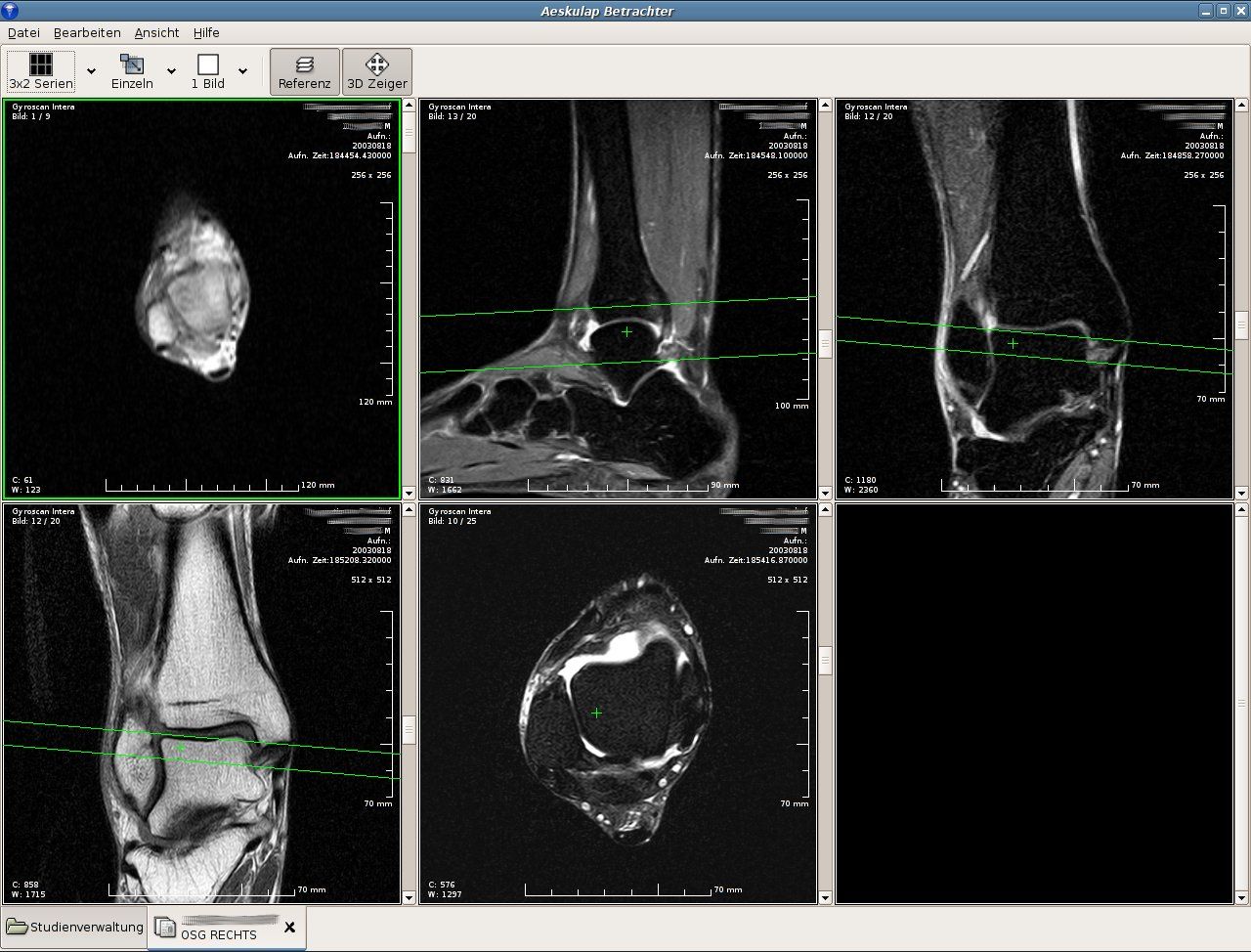
Aeskulap is a very famous DICOM mmanager/ and viewer on Ubuntu/ Debian linux.
Platform : Linux
12 - NextCloud : Cloud based DICOM Viewer
NextCloud is a free opensource self-hosted cloud file sharing solution, It provides security, solid user management and set of desktop and mobile clients which support synchronisation. NextCloud AppStore has DICOM viewer which is full featured DICOM viewer ready to work for teams and hospitals.
Platforms
- Server : Linux, Clients : Mac OSX, Windows, Linux. Mobile Apps Android and iPhone, web browsers desktop and mobile.
13 - Athena DICOM Viewer
Free DICOM viewer

Athena is a lightweight DICOM software, designed to display DICOM images on Windows machines. It's available in the Windows app store and offers an in-app purchase for additional options an features. Athena has a very simple custom design built for touch screens including Windows Tablets and wide resolution touch screens. Athena Lite edition comes with one month free for Athena pro editions which can be extended later with purchase. Athena was built by native windows technology so it's expected to be memory wise with smooth performance.
14 - ClearCanvas DICOM server and DICOM Viewer
ClearCanvas is an open source medical imaging project featuring DICOM server and features-rich DICOM viewer for Windows with DICOM viewer.
15- MatrixUser
MatrixUser is a lightweight GUI-based program for multi-dimensional data processing and analysis for medical imaging.
- Highly Interactive Graphical User Interface
- Multi-dimensional Matrix Display and Analysis in Matlab
- Multiple Data Type Conversion for DICOM, DICOM (Batch), NIFTI, MAT and Binary
- Nice DICOM Viewer and Convertor
- ROI Analysis, Segmentation, 3D Slicer and More Functions
16- Miele-LXIV: Open source DICOM Workstation for MacOSX

Miele-LXIV is an open source DICOM workstation and viewer for Mac OSX, It's completely native solution built by apple technologies, It supports 10.9 macOSX version and later, which means it'll work on old Mac OSX machines.
Miele-LXIV has many features that we have covered in this review.
Miele-LXIV is a Mac OSX [/10-dicom-viewers-for-mac-osx/] native DICOMworkstation and viewer, It’s completely free/ libre software as it releasedunder GPL3.0 license. Miele-LXIV is developed and maintained by group ofdevelopers who is providing regular upgrade for it. Miele-LXIV is available for …

17- SIVIC: Open source DICOM MR Spectroscopy Framework for Researchers, and Radiologists
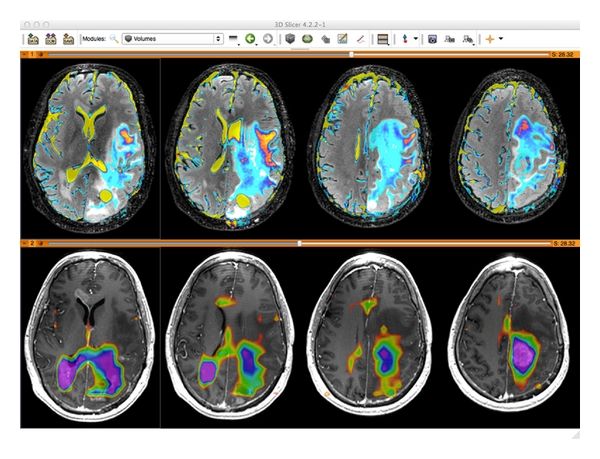
SIVIC: Open source DICOM MR Spectroscopy Framework for Researchers, and Radiologists
SIVIC is a customised DICOM MR Spectroscopy framework for researchers and radiologists, created by Nelson Lab.
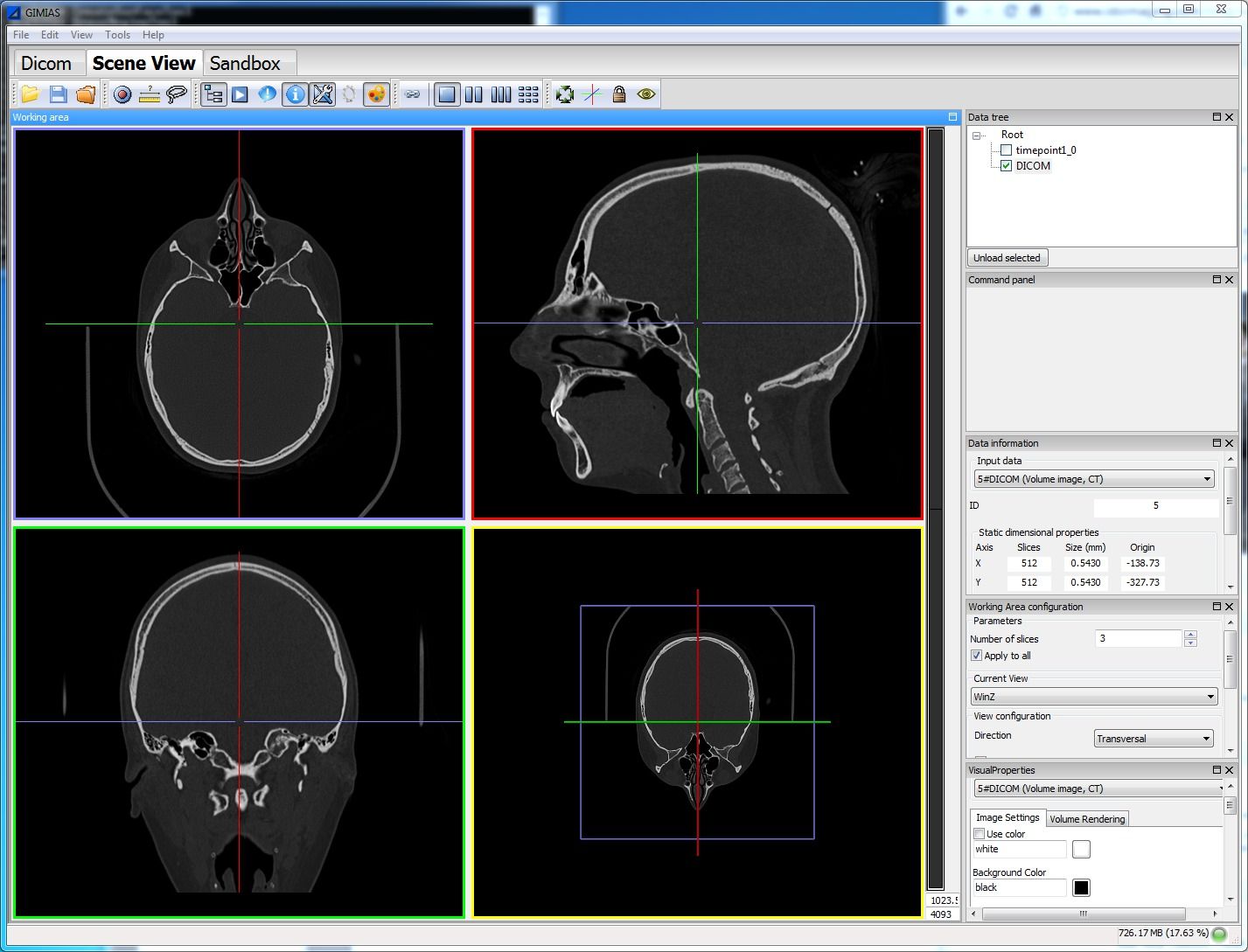
Gimias: is an open source framework for building medical Imaging & medical simulation applications for Windows and Linux
19- Yakami DICOM tools:
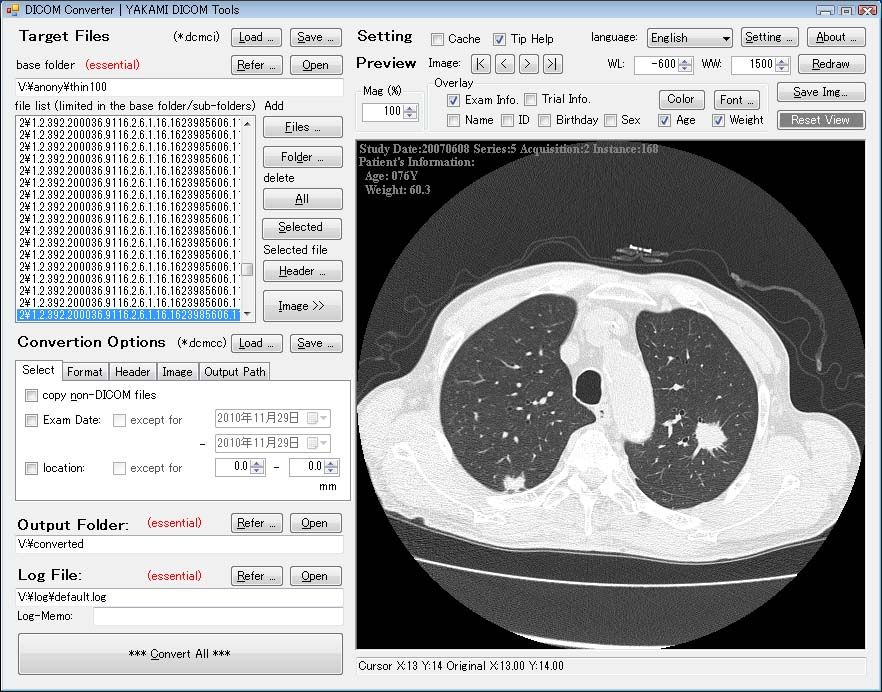
Yakami Converter
YAKAMI DICOM tools is a free lightweight DICOM viewer, & converter for Windows, we have reviewed it here.
Highlights
- Lightweight
- Easy to install, & use
- Works smoothly on old and new machines/ systems
- Suitable for novice users, & advanced users
- Supported languages: English, Japanese
20- Navegatium: (Windows)

Navegatium
Navegatium is a Free 2D/3D DICOM Viewer with 3D Printing support for Windows. It's full-featured DICOM viewer and PACS workstation for Windows, it supports Windows 7 and later.
Navegatium comes with full touch support for Windows-tablets, We have written a full review about it in here.
Highlights:
- DICOM / PACS Client
- 3D Printing on demand
- 3D Volume rendering
- Reports generation
- Navegatium Knowledge Base: Huge library of DICOM images
Navegatium's Homepage
21- JimboDICOMViewer

JimboDICOMViewer is a free 2D/ 3D DICOM viewer to display and manage DICOM datasets and databases. It has unique features, but it's available only for Linux and macOS.
Hospital Information Systems (HIS)/ EMR with DICOM viewer
Some Hospital Information systems are built with DICOM viewer to ensure the usability for DICOM files. Here is a list of free open-source hospital information systems some comes with complete DICOM and PACS integration.
Read also:
- 10+ Open source DICOM viewers and workstations ( Windows, Linux and Mac OSX ) .
- 10 Open source DICOM/ PACS Servers
DICOM (Digital Imaging and Communications in Medicine) is the international standard to transmit, store, retrieve, print, process, and display medical imaging information.

> Note: This article is an Evergreen [/tag/evergreen/] article. It will receivecontinues update about the listed applications. You can save it and return to itas a updated resource. What’s PACS? PACS in medicine stands for Picture Archiving and Communication System (PACS) amedical imaging tech…

> Note: This article is an Evergreen [/tag/evergreen/] article. It will receivecontinues update about the listed applications. You can save it and return to itas a updated resource.Some people feel comfortable using open source software, or dare I say feel“Free”, Medical programs are not diffe…

> Note: This article is an Evergreen [/tag/evergreen/] article. It will receivecontinues update about the listed applications. You can save it and return to itas a updated resource.Finding the right DICOM viewer is hard, there are plenty of commercial paidprograms come with different features, o…
Nowadays Many doctors and medical professionals prefer Mac OSX, Though findingmedical open source/ free professional software is not easy task, which forcesmany users into commercial solutions, That’s ok if the user is located a countrywith such software service provider as US, but for other co…
HIS stands for Hospital Information System which is integrated solution designed to manage all the hospital’s operations including medical operations, clinical workflow , financial , administrative,

Note: This article is an Evergreen article. It will receive continuous updates about the listed applications. You can save it and return to it as a updatedresource. -------------------------------------------------------------------------------- There are many commercial paid programs for perso…

Accounting is a major process in any sort of business, It’s even a major part ofour lives as for managing personal expenses and personal business operations. Many sectors oriented open source solutions, has integrated accounting modulesand extensions, so as ERP solutions which base their ERP syst…

Some people feel comfortable using open source software, or dare I say feel "Free", Medical programs are not different, however there is difficulty finding open source DICOM software in one place to help them decide and use the best alternatives to the commercial paid solutions.
We have covered several DICOM viewers categories, here what we have covered so far:
Why open source?
- Community powered
- Cost-effective
- Free alternative
1- AMIDE

AMIDE DICOM viewer on Linux - src
AMIDE, was my favorite when I used to be a regular daily Linux user, It's a smooth features-rich DICOM solution. It supports DICOM formats alongside other formats most of them are old but still used around the world.
AMIDE has powerful viewing and displaying tools for DICOM images, but its real power lays in importing, exporting and printing. It can import multiple data sets and raw data files as 8bit,16bit,32bit, float, imports also Acr/Nema 2.0, Analyze (SPM), DICOM 3.0, InterFile3.3, ECAT 6/7, and Gif87a/89a. It has movie generation option, and export studies as XML readable files.
2-Open DICOM viewer

Open DICOM Viewer
Open DICOM Viewer is a cross-platform DICOM application. It is a lightweight and is portable can work standalone directly from the CD/DVD and removable media. It supports web view display to display DICOM on web-page using Java technologies. It was built using Java, so it works on Windows, Mac OSX and Linux.
Though, Open DICOM viewer was not updated since 2015, but it is still getting many downloads and active users around the world.
3-SMILI

SMIL (Simple Medical Imaging Library Interface)
SMIL ( Simple Medical Imaging Library Interface ) is not just a DICOM viewer, It's a complete medical imaging visualization kit, SMIL is supporting wide range of medical imaging file extensions , starting with DICOM extensions as *.dcm, .dicom, ima, Nifti (.nii.gz .nii) and GIPL (.gipl) Analyse (.img *.hdr) Raster multimedia formats: PNG, JPEG, BMP, TIFF, PPM. SMIL also supports 3D models and extensions as ( *.vtp *.vtk *.ply *.obj *.stl ).
SMILI is packaged by video tutorials for the doctors , and an extensive documentation for developers including API documentation.
SMIL it was built by Python/ C++ and released under BSD 3-Clause License.
4-DicomPyler

DicomPyler DICOM viewer on Mac OSX. src
DicomPyler is a lightweight DICOM viewer, It works well on multiple operating systems, It supports remote DICOM viewing.
DicomPyler views CT/MR/PET images, disable DICOM tree structure, and provide patient anonymizer display set. DicomPyler was written using Python, and released under BSD license.
Platforms: Windows, Mac OSX and Linux
5- xMedCon
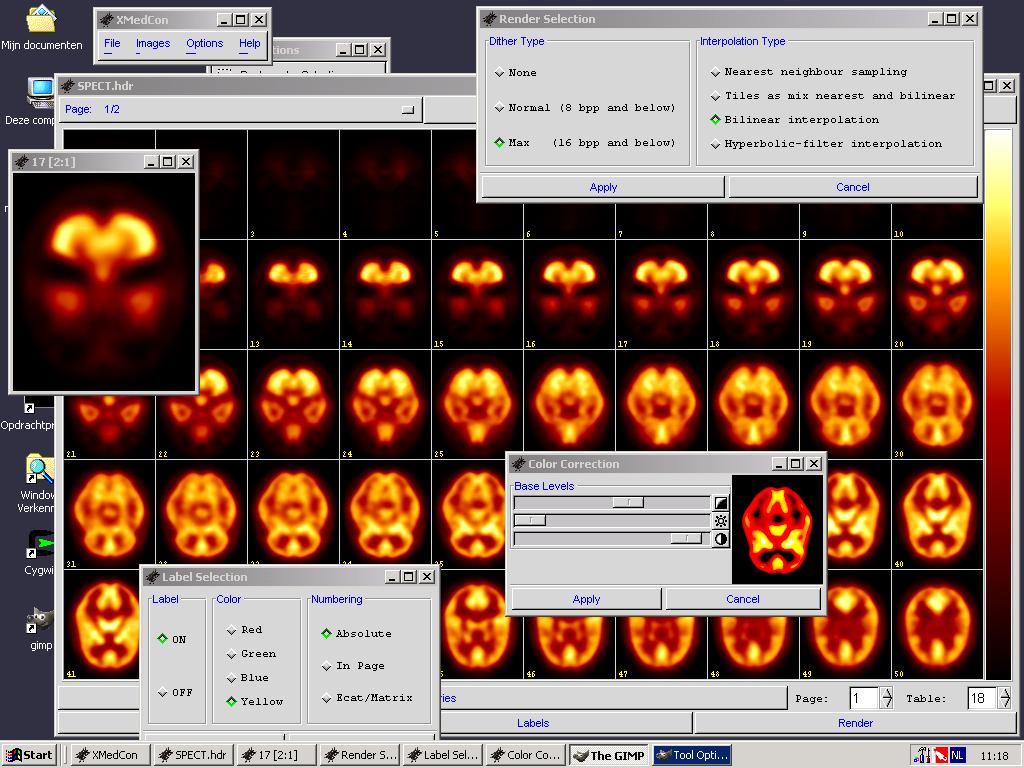
xMedCon DICOM Viewer (Windows, Linux, Mac OSX)
xMedCon is a DICOM viewer that provides DICOM images conversion functionality, It was written with C language and works flawlessly, It gives the user the option as well to export to jpg still image or gif animated image. xMedCon library has been used in several projects and proven to be a powerful base for DICOM related projects.
xMedCon has installation packages for Windows, Mac OSX, Linux ( Centos and Fedora ), Sabayon Linux, Debian, and FreeBSD systems.
6- Weasis
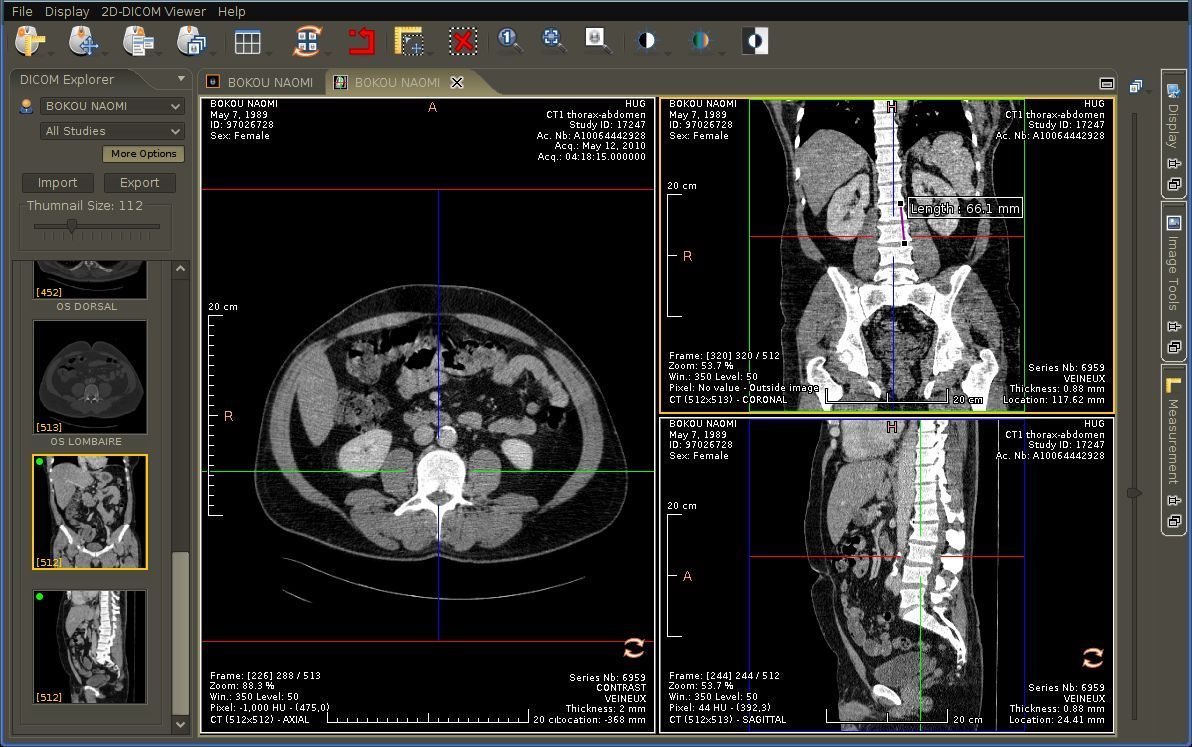
Weasis: Open source DICOM viewer
Weasis is a powerful standalone and web viewer DICOM workstation, It was built to manage DICOM workstations for hospitals, It utilizes OpenCV library which is a powerful CV ( Computer Vision ) programming library, and uses it to render and process the medical images. Weasis supports PACS servers. Weasis runs on Windows, Mac OSX and Linux. Weasis has a user-friendly interface and highly customizable. It supports multiple languages, themes, and multi-touch features.
Weasis released as an open source under Eclipse Public License (EPL).
7- Ginkgo CADx

Ginkgo CADx on Windows src
Ginkgo CADx is a DICOM viewer built to work on Windows, Linux and Mac OSX, It supports converting images like jpeg, pdf, tiff and png to DICOM formats. It supports many ( not all ) PACS servers and many modalities. It was released under GPL 3.0 license and begin used by doctors all over the world for years.

3DimViewer is a features-rich DICOM viewer program, It works on multiple operating systems. It's released as an open source project under Apache License v2.0.
3DimViewer supports 3D visualization and smooth 3D surface rendering, DICOM dataset imports, Volume rendering using graphics cards as NVidia or ATI, Multiplanar, and orthogonal XY, XZ and YZ views, multiple image manipulation tools.
9-DICOM Viewer & Editor

DICOM Viewer & Editor: DICOM tags editor and manage
This DICOM viewer has been developed using Qt library with Qt Creator on Linux, It has easy and simple user-interface. DICOM Viewer & Editor ( Yes that's its name ), allow the user to view and modify DICOM tags on single or multiple files, dump DICOM tags in single file and of course display DICOM files.
10- Horos ( Open source DICOM viewer for Mac OSX )
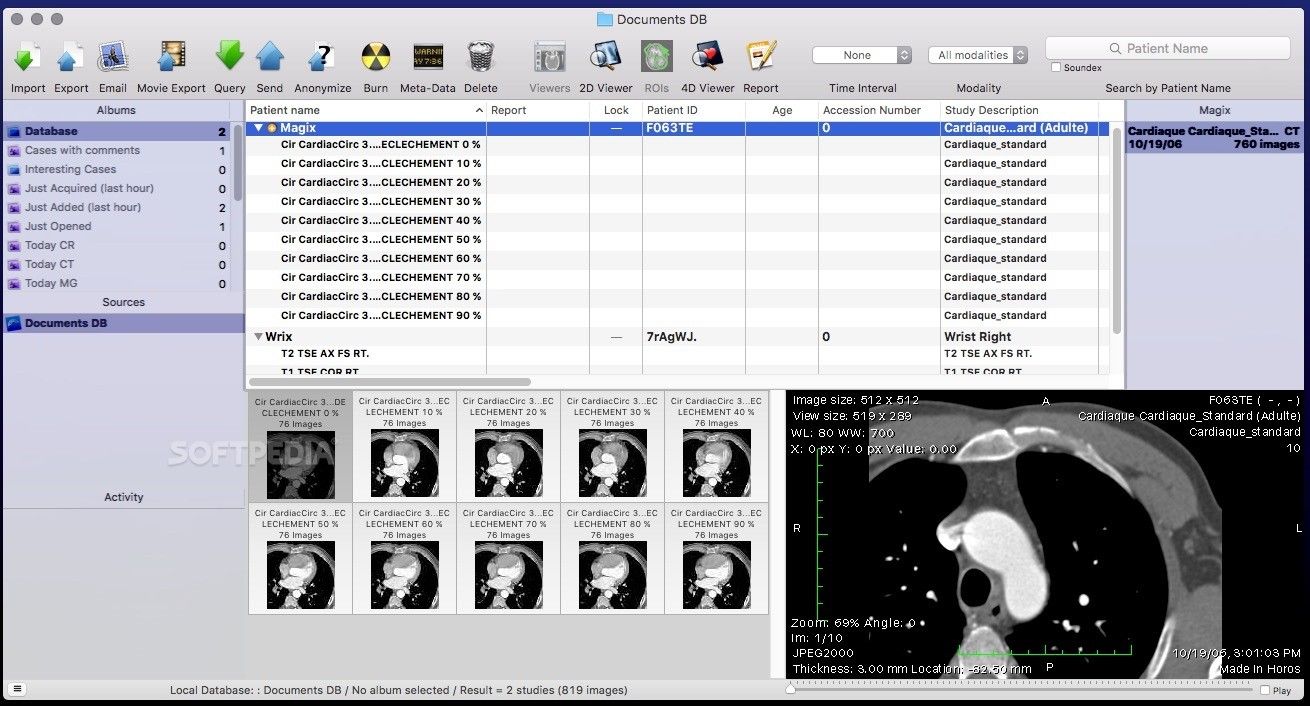
Horos (Open source DICOM viewer for Mac OSX)
Horos is a DICOM viewer for Mac OSX, it was released as an open source under GPL 3.0 license. It's features-rich DICOM viewer built for professional use. It was built on top of Osirix. We have published a snap review about Horos in here
11- ClearCanvas
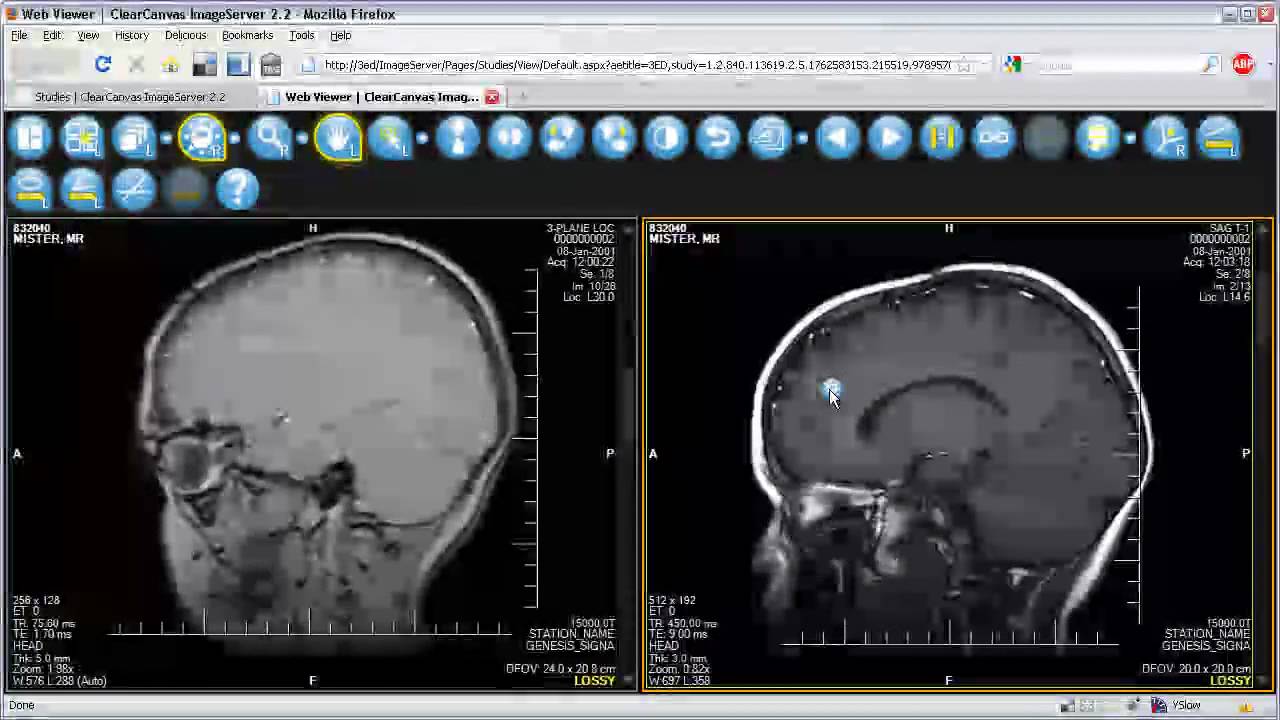
ClearCanvas is an open source & free DICOM viewer for Windows
ClearCanvas is an open source & free DICOM viewer for Windows, It supports the latest Windows version Windows 10, It also supports older version releases.
12- Miele-LXIV

Miele-LXIV in action
Miele-LXIV is a native build DICOM Workstation/ Viewer for Mac OSX. It supports old macOSX version and has many advanced features that sets it to compete with the enterprise DICOM workstation for Mac OSX.
13- DicomBrowser: Batch DICOM editor and browser

DicomBrowser is lightweight cross-platform DICOM batch editor and viewer. It has many functionalities that helps the users to batch edit DICOM tags for thousands of files at once.
14- JimboDICOMViewer
JimboDICOMViewer is an open source DICOM viewer and a DICOM convertor. It's available for all Linux distros that supports Snap Package manager. It's also available for Windows.
Free DICOM Viewer for Windows!
If you are looking for free DICOM viewers for Windows, We have created a list for that here (20 Free DICOM viewers for Windows)

PACS stands for Picture Archiving and Communication System, a medical imaging technology which provides economical storage and convenient access to images from multiple modalities.
DICOM (Digital Imaging and Communications in Medicine) is a standard for handling, storing, printing, and transmitting information in medical imaging. It includes a file format definition and a network communications protocol.
DICOM Workstation works as an option for most medical imaging equipment. It enables healthcare professionals to efficiently display and analyze digital medical images. It can receive digital images from PACS server or virtually any imaging modality including x-rays, MRIs, CTs, and more. It allows remote diagnostic and intensive interpretation of acquired images.
Best Free PACS Clients & DICOM Workstations:
1- Weasis

Weasis is a powerful standalone and web-based DICOM viewer. It was built to manage DICOM workstations for hospitals. It utilizes OpenCV library which is a powerful CV (Computer Vision) programming library, and uses it to render and process the medical images.
Weasis supports PACS servers. It has a user-friendly and highly customizable interface. It supports multiple languages, themes and multitouch features.
Weasis is released as an open source under Eclipse Public License (EPL).
Highlights:
- User-friendly and highly customizable interface
- Multitouch features
- Support for PACS servers
Platform: Windows, Mac and Linux.
2- 3D Slicer

3D Slicer, a free and open-source platform for analyzing and understanding medical image data. Built over two decades through support from the National Institutes of Health and a worldwide developer community. Slicer brings free, powerful cross-platform processing tools to physicians, researchers, and the public.
Slicer is built and tested on many hardware and software platforms. 3D Slicer runs on modern Windows, Mac OS X (10.7 and up), and a variety of Linux distributions.
Highlights:
- Bidirectional interface for devices
- Extensible, with powerful plug-in capabilities for adding algorithms and applications
- Manual segmentation of volumes
- Support for multi-modality imaging including, MRI, CT, US, nuclear medicine, and microscopy
- Interactive visualization of 3D image data
- Python Scripting
Platform: Windows, Mac and Linux.
3- Horos

Horos is a DICOM viewer for Mac OS X. It was released as an open source under GPL 3.0 license. It is a feature-rich DICOM viewer built for professional use. It was built on top of Osirix. We have published a snap review about Horos in here.
Highlights:
- Simple install, and zero configuration
- Plugins manager
- Effortless and simple Preferences/Settings Manager
- DICOM Query
Platform: macOS
4- Navegatium

Navegatium is a free DICOM Viewer for Windows 8.1 and Windows 10. It supports Touch Screens and can be installed directly from Windows Store.
It can visualize, analyze and manage DICOM files. It can access image files from removable media, a local drive or a PACS server. It also has integration with PACS (Picture Archiving and Communication System) for hospitals, clinics and research centers, allowing doctors, radiologists, pathologists and researchers consult and store their studies and medical imaging in their work institutions.
We have written a snap review listing all the features of Navegatium, you can read about it in here.
Highlights:
- DICOM / PACS-ready
- 3D Printing on demand
- 3D Volume rendering
- Reports generation
- Navegatium Knowledge Base: Huge library of DICOM images
- Support for Touch-screens
Platform: Windows 8.1 or Windows 10.
5- Aliza
Aliza is a DICOM viewer that supports multiple modalities and formats. It has been released for Windows and Linux (Debian, Ubuntu, Fedora, and Redhat). Aliza is in active development, and it is getting often upgraded by an active team of developers. Aliza supports 3D and 2D format.
Highlights:
- DICOM Structured Report browser
- DICOM Dictionary (Data Elements and UIDs)
- Directory scanner
- Siemens Mosaic format
- Kretztechnik (Kretz) volume format (partial support)
Platform: Windows and Linux.
6- Miele-LXIV

Miele-LXIV is a Mac OS X native DICOM workstation and viewer. It's completely free/libre software as it is released under GPL3.0 license. Miele-LXIV is developed and maintained by group of developers who are providing regular upgrade for it.
Miele-LXIV is available for install from the iTunes app store (macApp) which makes it easy to follow its releases and upgrade to the latest release with one click.
Miele-LXIV has a plugin generator that allow developers to build their plugins quickly using Xcode.
Highlights:
- Intuitive GUI
- 4D Viewer for Cardiac-CT and other temporal series
- Plugins support for external functions
- Plugin generator
- Export any 3D images to QuickTime, TIFF, JPEG
- Built-in SQL compatible database with an unlimited number of files
- Query and Retrieve studies from/to a PACS workstation (C-FIND SCU, C-MOVE SCU, WADO)
- Multithreaded for multiprocessors and multicore processors support
Platform: macOS
Website: URL
7- Ginkgo CADx
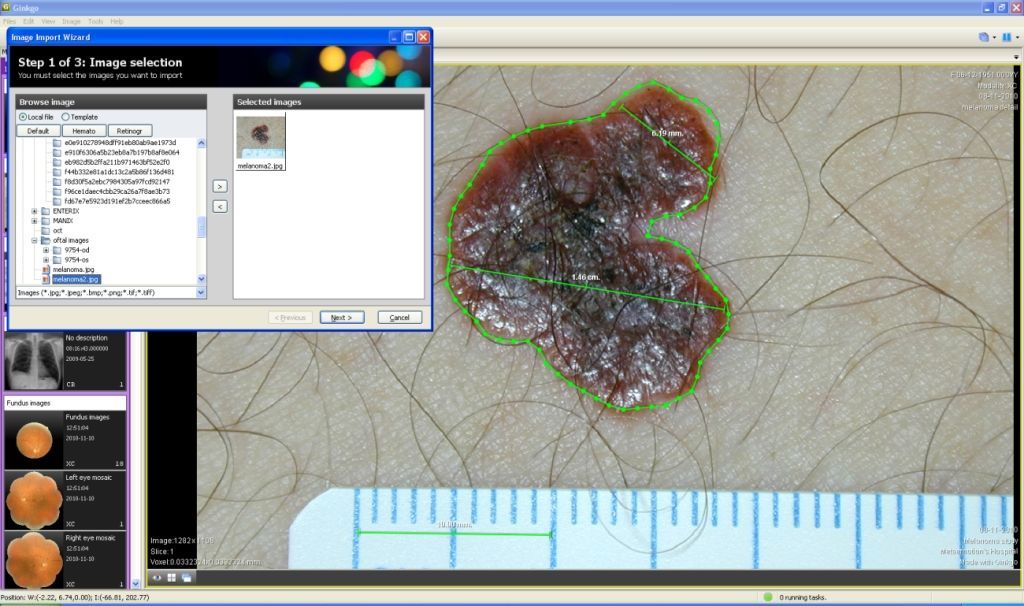
Ginkgo CADx is an advanced DICOM viewer and dicomizer (converts PNG, JPEG, BMP, PDF, tiff to DICOM). It has simple user-interface but advanced features designed for radiologists. Ginkgo is in active development, and it has been released as an open source for personal and commercial use under GPL3 license. It offers Windows, Linux and Mac OSX installation packages.
Highlights:
- Dicomization support from JPEG, PNG, GIF and TIFF
- PACS Workstation (C-FIND, C-MOVE, C-STORE. )
- Multiple modalities support (Neurological, Radiological, Dermatological, Ophthalmological, Ultrasound, Endoscopy, . )
- Automatic retinal analysis diagnostics, Psoriasis automatic diagnostics and Retinal image mosaic composition through custom extensions
Platform: Windows, Mac and Linux.

SMILI (Simple Medical Imaging Library Interface) is an open-source, light-weight and easy-to-use medical imaging viewer and library for all major operating systems. The main sMILX application features for viewing n-D images, vector images, DICOMs, anonymizing, shape analysis and models/surfaces with easy drag and drop functions. It also features a number of standard processing algorithms for smoothing, threshold, masking etc. images and models, both with graphical user interfaces and/or via the command-line.
Highlights:
- DICOM and DICOM RT support
- n-D Image Visualization
- Animating Surfaces
- Polygonal Contouring
- Shape Modelling
- Python Scripting
Platform: Windows, Mac and Linux.
9- Mango
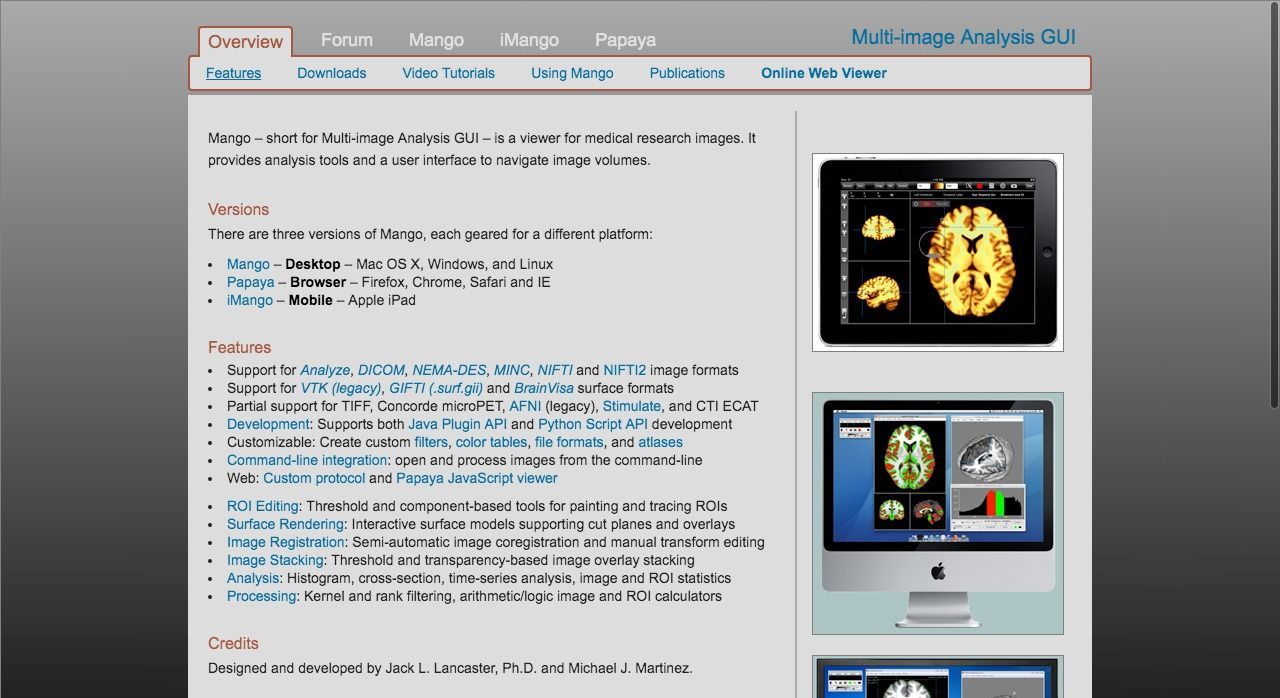
Mango is a free cross-platform DICOM program that supports multiple unique formats as well as DICOM images. It is available for use as a free software for non-commercial use. It is developer-friendly with nice and easy user-interface. It supports developers to build and extend it with powerful scripting languages as Python and Java. It is highly modular and extensible with plugins and modules.
Highlights:
- Support for Analyze, DICOM, NEMA-DES, MINC, NIFTI and NIFTI2 image formats
- Support for VTK (legacy), GIFTI (.surf.gii) and BrainVisa surface formats
- Partial support for TIFF, Concorde microPET, AFNI (legacy), Stimulate, and CTI ECAT
- Histogram, cross-section, time-series analysis, image and ROI statistics
- Behavioral Analysis, Disease Analysis, Paradigm Analysis, Extract Brain (Separate brain from non-brain tissue) and more functionalities through plugins
- Plugin Manager
- Support for Java Plugin API and Python Script API development
Platform: Windows, Mac and Linux.
10- MicroDICOM

MicroDicom is an application for primary processing and preservation of medical images in DICOM format.
It is equipped with most common tools for manipulation of DICOM images and it has an intuitive user interface. It is free for non-commercial use.
Highlights:
- Intuitive user interface
- Structures Reports, MPEG-2 and MPEG-4 transfer syntaxes, Encapsulated PDF
- DICOM viewer portable version
- Measurements and annotations
Platform: Windows.
Conclusion
There are many free and great DICOM/PACS Programs, but we think that Weasis (Windows, Mac and Linux), 3D Slicer (Windows, Mac and Linux), Horos (Mac) and Navegatium (Windows 8.1 or above) are the best choices due to their features and active development.
Сегодня мне бы хотелось пролить свет на одну из самых неосвещённых тематик на хабре. Речь пойдёт о визуализаторе медицинских радиологических изображений или DICOM Viewer'е. Планируется написать несколько статей, в которых поговорим об основных возможностях DICOM Viewer'а — в том числе возможности воксельного рендера, 3D, 4D, рассмотрим его устройство, поддержку протокола DICOM и др. В этой статье я расскажу о воксельном рендере и его устройстве. Всем заинтересовавшимся добро пожаловать под кат.

Компания, в которой я работаю, имеет большой опыт в сфере разработки программного обеспечения медицинской направленности. С некоторыми проектами мне довелось работать, поэтому хотелось поделиться накопленным опытом в этой области и показать, что у нас получилось. Также хотелось бы воспользоваться случаем и получить обратную связь от врачей-ренгенологов по использованию Viewer'а.
Одним из наших продуктов является DICOM Viewer — просмотрщик медицинских изображений формата DICOM. Он умеет рендерить 2D изображения, строить 3D модели на основе 2D слайсов, а также поддерживает операции как для 2D изображений, так и для 3D моделей. Об операциях и возможностях Viewer'а я напишу в следующей статье. В конце статьи будут указаны ссылки на сам DICOM Viewer с полным функционалом, который описан в статье и на данные для проб. Но всё по порядку.
Представление изображений в медицине
Чтобы представлять как построить 3D-модель, например, головного мозга, из 2D DICOM-файлов, нужно понимать как представлены изображения в медицине. Начнём с того, что все современные томографы (МРТ, КТ, ПЭТ) не производят готовых изображений. Вместо этого формируется файл в специальном формате DICOM, который содержит информацию о пациенте, исследовании, а также информацию для отрисовки изображения. Фактически каждый файл представляет срез (slice) произвольной части тела, в какой-либо плоскости, чаще всего в горизонтальной. Так вот каждый такой DICOM-файл содержит информацию об интенсивности или плотности тканей в конкретном срезе, на основе которой строится итоговое изображение. На самом деле интенсивность и плотность — это разные понятия. Компьютерная томография сохраняет в файлах рентгеновскую плотность, которая зависит от физической плотности тканей. Кости имеют большую физическую плотность, кровь меньшую и т.д. А магнитно-резонансный томограф сохраняет интенсивность обратного сигнала. Мы же будем применять термин плотности, обобщая таким образом выше описанные понятия.
Информацию о плотности в DICOM-файле можно представить в виде обычного изображения, у которого есть разрешение, размер пикселя, формат и другие данные. Только вместо информации о цвете в пикселе храниться информация о плотности тканей.
Диагностическая станция производит не один файл, а сразу несколько для одного исследования. Эти фалы имеют логическую структуру. Файлы объединяются в серии и представляют собой набор последовательных срезов какого-либо органа. Серии объединяются в стадии. Стадия определяет всё исследование. Последовательность серий в стадии определяется протоколом исследования.
2D-рендер
Информация о плотности тканей в DICOM-файле является основой для его отрисовки. Чтобы отрисовать изображение нужно значениям плотности сопоставить цвет. Это делает передаточная функция, которую в нашем viewer'е можно редактировать. Кроме того есть множество готовых пресетов для отрисовки разных по плотности тканей разными цветами. Вот пример передаточной функции и результат отрисовки:

На графике обозначены две точки белого цвета на концах белой линии, что говорит о том, что будет рисоваться только белый цвет. Линия, соединяющие точки, обозначает непрозрачность (opacity), т.е. менее плотные ткани отрисовываются более прозрачными пикселями. Таким образом белый цвет плюс соответствующее значение непрозрачности даёт градации белого, что и видно на картинке. В данном примере показана относительная передаточная функция, поэтому по оси абсцисс отложены проценты. Синим цветом на графике показано распределение плотностей тканей, где каждому значению плотности соответствует количество пикселей (вокселей), приходящихся на данную плотность.
В нашем рендере происходит отрисовка белого цвета с соответствующей прозрачностью на чёрном фоне, чёрный цвет никогда не отрисовывается. Такая схема удобна при отрисовке 3D-модели — воздух имеет небольшую плотность, следовательно отрисовывается прозрачным, поэтому при наложении слайсов через воздух наложенного изображения будет видно нижнее. К тому же, если бы цвет имел не константную характеристику, а линейную (чем характеризуется переход от чёрного цвета к белому), то при перемножении цвета на прозрачность (которая также имеет линейную характеристику) получилась бы квадратичная характеристика, которая отражала бы цвет иначе, что не является верным.
Передаточные функции разделяются по типу на абсолютные и относительные. Абсолютная передаточная функция строится для всех возможных плотностей. Для КТ это шкала Хаунсфилда (от -1000 до ~3000). Плотность равная -1000 соответствует воздуху, плотность, равная 400, соответствует костям, нулевая плотность соответствует воде. Для плотностей по шкале Хаунсфилда верно следующее утверждение: каждая плотность соответствует определённому типу ткани. Однако для МРТ это утверждение не верно, поскольку МР-томограф для каждой серии генерирует собственный набор плотностей. То есть для двух серий одна и та же плотность может соответствовать разным тканям тела. В абсолютной передаточной функции аргументы соответствуют абсолютным значениям плотности.
Относительная передаточная функция строится на основе так называемого окна, которое указывает какой именно диапазон плотностей нужно отрисовывать. Окно определяется параметрами Window Width (W) и Window Center (L), рекомендуемые значения которых задаются томографом и сохраняются в файлы-снимки в соответствующих DICOM-тэгах. Значения W и L могут быть изменены в любой момент. Таким образом, окно ограничивает область определения передаточной функции. В относительной передаточной функции аргументы соответствуют относительным значениям, заданным в процентах. Пример передаточной функции показан на рисунке выше со шкалой в процентах от 0 до 100.
Как в случае абсолютной, так и в случае относительной передаточной функции возможны случаи, когда передаточная функция покрывает не все плотности, содержащиеся в файле-снимке. В этом случае все плотности, которые попадают справа от передаточной функции принимают значения самого правого значения передаточной функции, а плотности слева — самого левого значения передаточной функции соответственно.
Пример абсолютной передаточной функции, в которой плотность задана в абсолютных значениях по шкале Хаунсфилда:

Вот пример более сложной передаточной линейной функции, окрашивающей плотности в несколько цветов:

Как и на предыдущем рисунке прозрачность имеет линейную характеристику. Однако для конкретных плотностей заданы цвета. Помимо цвета каждая из этих точек определяет прозрачность (в соответствии с белой линией на графике). В случае 3D-модели каждая из точек также хранит отражательные компоненты. Между конкретных точек производится интерполяция отдельно для каждой компоненты, включая прозрачность, RGB, отражательные компоненты, получая таким образом значения для остальных плотностей.
Прозрачность в передаточной функции не обязательно должна быть линейной. Она может быть любого порядка. Пример передаточной функции с произвольной прозрачностью:

Помимо прочего, на каждом 2D-изображении отрисовывается информация об изображении. В правом нижнем углу рисуется куб ориентации, по которому можно понять как расположен пациент в данном изображении. H – head (голова), F – foot(ноги), A – anterior (анфас), P – posterior(спина), L – left(левый бок), R – right(правый бок). Эти же буквы дублируются в середине каждой из сторон. В левом нижнем и правом верхнем углах для врачей-ренгенологов отображается информация о параметрах томографа, с которыми было получено данное изображение. Также справа рисуется линейка и масштаб одного деления соответственно.
Воксельный рендер
Что это ?
Посколько воксельный рендер является основой для нескольких наших проектов, он представлен в виде отдельной библиотеки. Она называется VVL(анг. Volume Visualization Library). Она написана на чистом С без использования каких-либо сторонних библиотек. VVL предназначена для рендеринга трёхмерных моделей, построенных из данных DICOM-сканеров (МРТ, КТ, PET). VVL использует все преимущества современных многоядерных процессоров для realtime-отрисовки, поэтому может работать на обычной машине, а также имеет реализацию на CUDA, что даёт гораздо более высокую производительность, чем на CPU. Вот пара изображений, полученного рендером на основе данных компьютерной томографии.


В VVL реализован весь процесс отрисовки, начиная с построения модели и заканчивая генерированием 2D изображения. Есть такие фишки как ресэмплинг, антиалиасинг, полупрозрачность.
Воксельная модель изнутри
Воксель — это элемент объёмного изображения, содержащего значение элемента в трёхмерном пространстве. В качестве значения вокселя в общем случае может выступать что угодно, включая цвет. В нашем случае в качестве значения вокселя выступает плотность. Что касается формы вокселя, то в общем случае воксели могут быть кубическими, или представлять собой параллелепипед. У нас воксели представлены в виде кубов для упрощения и удобства работы. Координат воксели не хранят, они вычисляются из относительного расположения вокселя.
По сути, воксель является полным аналогом пикселя в 3D. Pixel (англ. picture element) — элемент изображения,Voxel (англ. volume element) – элемент объёма. Практически все характеристики пикселя переносятся на воксель, поэтому можно смело проводить аналогии, учитывая размерность. Таким образом, воксели используются для представления трёхмерных объектов:

На скриншоте можно разглядеть маленькие кубические воксели. Для хранения плотности в вокселе используется 2х байтовое число. Поэтому можно вычислить размер модели: 2 байта на плотность * количество вокселей. Некоторые воксельные рендеры, помимо сказанного, хранят в вокселе информацию для рендеринга, что требует дополнительной памяти. Практически нами было установлено, что это нецелесообразно и нужные данные выгоднее вычислять «на лету», чем хранить лишние байты.
Представление модели в памяти

Поскольку протоколом DICOM чётко не декларируется, в каком тэге хранится величина расстояния между изображениями в серии, приходится вычислять расстояние между изображениями по другим данным. Так, каждое изображение имеет координаты в пространстве и ориентацию. Этих данных достаточно, чтобы определить расстояние между изображениями. Таким образом имея разрешение изображения и расстояние между ними в серии, можно определить размер вокселя. Разрешение изображения по X и Y, как правило, одинаковое, т.е. пиксель имеет квадратную форму. А вот расстояние между изображениями может отличаться от этого значения. Поэтому воксель может иметь форму произвольного параллелепипеда.
Для простоты реализации и удобства работы мы делаем ресемплинг для величины плотности, используя бикубическую фильтрацию (фильтр Митчелла), и получаем кубическую форму вокселя. В случае, если размер пикселя меньше расстояния между слайсами, то мы добавляем слайсы (supersampling), а если размер пикселя больше, то убираем слайсы (downsampling). Таким образом размер пикселя становится равным расстоянию между слайсами и мы можем построить 3D-модель с кубической формой вокселя. Проще говоря, мы подгоняем расстояние между изображениями к разрешению изображения.
Полученные воксели хранятся в структуре, представляющей собой массив, оптимизированный под доступ в произвольном направлении движения, в случае отрисовки на процессоре. Массив разбит логически на параллелепипеды, хранящиеся в памяти непрерывным куском размером ~1,5кб при размере вокселя 2 байта, что позволяет поместить несколько близко расположенных параллелепипедов в кэш процессора первого уровня. Каждый параллелепипед хранит 5х9х17 вокселей. Исходя из размера такого параллелепипеда рассчитываются координаты смещений в общем массиве вокселей и сохраняются в 3 отдельные массива xOffset, yOffset, zOffset. Поэтому обращение к массиву происходит так: m[xOffest[x] + yOffset[y] + zOffset[z]]. Таким образом, начиная читать данные в параллелепипеде, мы заставляем процессор положить весь параллелепипед в кэш процессора первого уровня, что ускоряет время доступа к данным.
В случае рендеринга на GPU используется специальная трёхмерная структура в графической памяти видеокарты, называемая 3D-текстурой, доступ к вокселям в которой оптимизируется средствами видеоадаптера.
Рендеринг
Рейтрейсинг — как способ рендеринга. Перемещаемся по лучу с некоторым шагом и ищем пересечение с вокселем и на каждом шаге проводим трилинейную интерполяцию, где 8 вершин представляют середины соседних вокселей. На CPU используется окто-дерево в качестве оптимальной структуры для быстрого пропуска прозрачных вокселей. На GPU для 3D-текстуры трилинейная интерполяция выполняется автоматически средствами видеокарты. На GPU не используется окто-дерево для пропуска прозрачных пикселей, поскольку в случае 3D-текстуры иногда оказывается, что быстрее учитывать все воксели, чем тратить время на поиск и пропуск прозрачных.
В качестве модели освещения используется затенение по Фонгу, которое позволяет сделать изображение объёмным и даёт хорошую картинку и в то же время не мешает работать врачам-ренгенологам. Рейтрейсинг производится с учётом прозрачности вокселей, что позволяет рендерить полупрозрачные ткани.
Рендер поддерживает режимы перспективной

и параллельной проекций

Перспективная проекция более реалистична. Более того, она необходима для виртуальной эндоскопии, о которой расскажу в следующей статье.
Читайте также:


